targeting sequence : secuencia
de acceso.
![]() leader
sequence.
leader
sequence.
TATA box: caja TATA.
Observación: en los organismos procariotas se
conoce con el nombre de «caja Pribnow» y en los eucariotas, con el
de «caja Hogness» . Ambas tienen en común el
tetranucleótido
TATA, de allí que se llamen a veces «cajas TATA». Véanse
Hogness box, Pribnow
box.
TATA element: caja TATA.
![]() tATA
box.
tATA
box.
template strand : cadena
plantilla, cadena molde.
1 Cadena de ácido nucleico que sirve de plantilla para
la síntesis de una cadena de ácido nucleico complementaria.
2 En la replicación de un ácido nucleico, es cualquiera
de las dos cadenas del ácido nucleico bicatenario (ADNbc, ARNbc)
que, al separarse, sirve de plantilla para la síntesis de una
cadena hija complementaria. Ambas cadenas de un ácido nucleico
bicatenario sirven de plantilla para la síntesis de sendas hebras
hijas.
3 En la transcripción, es sinónimo de «cadena
no codificante». Véase noncoding strand.
Observación: aunque la expresión template strand siempre
se utilizó como sinónimo de «cadena no codificante» (noncoding
strand), los recientes avances y aplicaciones de la biología
molecular exigen incluir aquí una acepción más
amplia que tome en consideración la copia de ADN o de ARN a
partir de ADN, y la de ARN o ADN a partir de ARN.
termination codon : codón
de terminación, codón de finalización de lectura,
codón de parada.
![]() stop
codon.
stop
codon.
terminator: terminador.
Secuencia de ADN bicatenario, contigua al extremo 3’ de un gen, que
posibilita la disociación de la ARN-polimerasa de la hebra de ADN
y la liberación de la hebra de ARN recién sintetizada dando
por finalizada la transcripción. Sólo permite la finalización
de la transcripción del gen precedente que ha sido previamente «recorrido» por
la ARN-polimerasa.
Observación: en las bacterias existen dos clases de terminadores,
los independientes de la proteína ρ (también llamados
terminadores intrínsecos) y los dependientes de ρ. Ambos afectan
a la polimerasa una vez que han sido transcritos (funcionan en el ARN y
no en el ADN). En los organismos eucariotas existen terminadores específicos
de las ARN-polimerasas I y III, pero los de la ARN-polimerasa II están
menos caracterizados.
TGS :TGS.
![]() transcriptional
gene silencing (TGS).
transcriptional
gene silencing (TGS).
trailer sequence : secuencia
remolque, secuencia trasera.
En los ARNm, es la secuencia de ribonucleótidos que se extiende
desde el codón de terminación hasta el extremo 3’ y
que, por consiguiente, no se traduce.
TRAM: TRAM.
![]() translocating
chain-associated membrane protein.
translocating
chain-associated membrane protein.
transactivator: transactivador.
Activador que interacciona de forma directa con la ARN- polimerasa (sin
la ayuda de coactivadores). Véase activator.
transcribed spacer : espaciador
transcrito, espaciador intragénico, espaciador.
Secuencia interna de una unidad de transcripción que se transcribe
y luego desaparece al madurar el ARN transcrito mediante uno o dos cortes
endonucleotídicos, sin empalme ulterior de los extremos producidos.
Son característicos de la maduración de los ARNr.
Observación: estos espaciadores no son intrones, pues
su eliminación no trae aparejado un empalme de exones, tal como
ocurre tras la escisión intrónica en el fenómeno
de corte y empalme. Tampoco se ha de confundir con un espaciador intergénico.
Véase non transcribed spacer y splicing.
transcribing strand : cadena
no codificante.
![]() noncoding
strand.
noncoding
strand.
transcript : transcrito.
Molécula de ARN transcrita a partir de una hebra complementaria
de ADN.
Observaciones: el DRAE recoge la palabra «transcrito» como
voz grave y no esdrújula y, por lo tanto, debe llevar acento prosódico
(pero no ortográfico) en la letra i.
transcription : transcripción.
Síntesis de ARN a partir de una hebra de ADN catalizada por la
ARN-polimerasa con el auxilio de proteínas específicas
(factores de transcripción). Comprende tres fases denominadas
iniciación (initiation), elongación (elongation)
y terminación (termination). En los organismos eucariotas
existen tres tipos de transcripción según la ARN-polimerasa
que la lleva a cabo: a) la transcripción de ARNr catalizada por
la ARN-polimerasa I, b) la transcripción de ARNm catalizada por
la ARN-polimerasa II, y c) la transcripción de ARNt y otros ARN
pequeños catalizada por la ARN-polimerasa III. En los organismos
procariotas existe sólo un tipo de transcripción y de ARN-polimerasa.
Véanse DNA-directed
RNA polymerase, noncoding
strand y RNA-polymerase.
transcription factor: factor
de transcripción.
Proteína necesaria para el inicio de la transcripción de
un gen, distinta de la ARN-polimerasa. Reconoce secuencias específicas
ubicadas en el interior de promotores y potenciadores y puede asociarse
con la ARN-polimerasa misma o con otros factores de transcripción,
o formar parte de un complejo de iniciación transcripcional únicamente
en presencia de otras proteínas.
transcription start point: inicio
transcripcional.
Nucleótido del ADN que marca el inicio de la cadena de ARN. Se
designa con el número +1.
transcription unit : unidad
de transcripción.
Segmento de ADN que se transcribe en una molécula de ARN mediante
una reacción enzimática catalizada por la ARN-polimerasa.
Observación: esta expresión se utiliza mucho con
referencia a los organismos procariotas, dado que en estos casos las
unidades de transcripción pueden contener uno o más cistrones
(es decir, varios genes). Es menos frecuente en relación con
los organismos eucariotas, habida cuenta de que los genes eucarióticos
son generalmente monocistrónicos (salvo quizás los genes
de los ARNr), de modo que una unidad de transcripción refleja
el ordenamiento de bases de un único gen. Véase cistron, gene y RNA polymerase.
transcriptional gene silencing (TGS): silenciamiento
génico transcripcional.
Bloqueo de la transcripción de un gen activo debido a la presencia
de secuencias homólogas (por ejemplo, ARNbc homólogos).
Se acompaña de metilaciones locales, usualmente en el promotor
del gen. Las metilaciones traen aparejados a su vez cambios estructurales
en la cromatina, que entonces se convierte en heterocromatina y pierde
la capacidad de transcribirse. Se trata de un fenómeno epigenético
estable y heredable. Véase RNA interference.
transcriptional unit : unidad
de transcripción.
![]() transcription
unit.
transcription
unit.
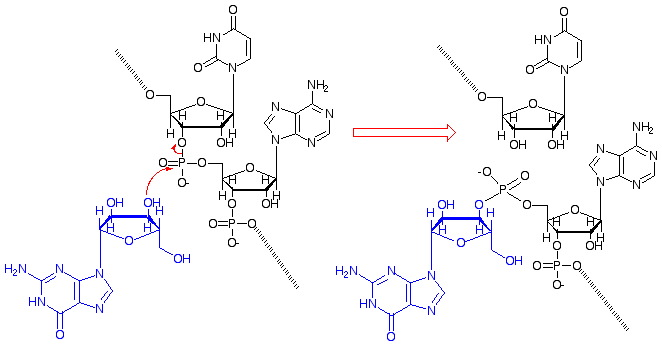
transesterification : transesterificación.
1 Reacción de un éster con un alcohol en presencia
de un catalizador en la que se intercambian grupos alcohólicos –es
decir, se forma un segundo éster y un segundo alcohol– sin
gasto de energía:
R-CO-OR’ + R’’OH g R-CO-OR’’ +R’OH
Las enzimas que catalizan estas reacciones son proteasas (tripsina,
quimotripsina, papaína, etc.) o esterasas.
2 En el ARN (véase la figura abajo), es la reacción
que se produce durante el fenómeno de corte y empalme en los
intrones de los grupos I, II y III; en este caso el grupo acilo es
el fosfato de unión de las dos ribosas, y los alcoholes intercambiados
son los del carbono 3’ de distintas moléculas de ribosa.
transfer RNA (tRNA) : ARN
de transferencia (ARNt).
Pequeña molécula de ARN (de tamaño inferior a 100
nucleótidos) que actúa de intermediario en la incorporación
de un aminoácido en el extremo carboxilo de un polipéptido
naciente durante la síntesis de una proteína. Suele dibujarse
en forma de trébol (con arreglo a su estructura secundaria), pero
adopta tridimensionalmente la forma de una letra L. En uno de los extremos
de la L lleva un anticodón de tres nucleótidos complementario
delcodón del ARNm, y en el otro, que coincide con el extremo 3’ de
la molécula, lleva unido un aminoácido por un enlace covalente
de tipo éster entre el hidroxilo 3’ del ARNt y el carboxilo
del aminoácido. Existe al menos un ARNt por cada aminoácido
natural, aunque un mismo aminoácido es capaz de interaccionar
con varios ARNt.
transformation: transformación.
Proceso de introducción de moléculas de ADN en el interior
de las células bacterianas. Se realiza fundamentalmente mediante
dos procedimientos distintos: con la ayuda de sustancias químicas
(dimetilsulfóxido, cationes Rb+ , Ca2+ , Co2+ ,
etc.) o mediante electroporación.
transit
peptide : péptido
de tránsito.
![]() leader
sequence.
leader
sequence.
transgene-induced co-suppression :cosupresión
inducida por transgenes.
![]() co-suppression,
RNA interference.
co-suppression,
RNA interference.
Observación: es un caso de ribointerferencia causada
por ARNbc de origen transgénico.
transgene silencing :silenciamiento
por transgenes.
![]() transgene-induced
co-suppression, co-suppression.
transgene-induced
co-suppression, co-suppression.
transition: transición.
![]() base-pair
substitution.
base-pair
substitution.
translational repression: represión
de la traducción.
Regulación temporal de la expresión de un gen durante el
desarrollo de un organismo eucarionte gracias a la presencia de pequeños
ARN monocatenarios denominados «ARN temporales pequeños» (ARNtp),
que se hibridan con los correspondientes mensajeros (ARNm) e inhiben
de este modo su traducción en proteína. Véase Dicer,
small temporal RNA.
translocase: translocasa,
transportador.
Tiene dos significados posibles:
1 translocase: translocasa. Véase EF-G
2 transporter: transportador. Véase porter.
translocating chain-associated membrane
protein: proteína de membrana asociada al
polipéptido de exportación.
Proteína transmembranaria del traslocón, que reconoce la
secuencia señal de la proteína en vías de exportación
después del SRP y estimula el traslado de la proteína al
interior del retículo endoplásmico.
Véase signal recognition particle (srp), signal
sequence y translocon.
translocation: translocación,
traslación, traslado.
Suele traducirse de distintas maneras según el contexto de uso:
1. Biol. mol. Traslación (del ribosoma): movimiento
de avance de tres nucleótidos en la cadena de ARNm que realiza
el ribosoma durante la síntesis de proteínas; su finalidad
es expulsar el ARNt libre del sitio P —sitio del peptidil-ARNt— para
permitir el ingreso del peptidil-ARNt recién formado. Con este
movimiento, el sitio A del ribosoma —sitio del aminoacil-ARNt— queda
también libre y listo para recibir el aminoacil-ARNt correspondiente
al próximo codón.
2. Biol. mol. Traslado (de solutos, de proteínas):
movimiento general de una molécula de un lugar a otro de la
célula, como puede ser el de un soluto o el de una proteína
a través de una membrana celular.
3. Gen. Translocación: mutación por la
cual un segmento cromosómico cambia de sitio dentro del mismo
cromosoma (ubicándose en el mismo brazo o en otro brazo) o se
traslada a otro cromosoma (homólogo o no homólogo). En
este último caso, el traslado puede ir acompañado o no
de un intercambio recíproco de segmentos entre cromosomas. La
translocación no recíproca (movimiento de un segmento
cromosómico hacia un lugar distinto dentro del mismo o de otro
cromosoma, sin intercambio de segmentos) recibe el nombre preferente
de «transposición». Véase transposition.
translocon: traslocón.
Canal de la membrana del retículo endoplásmico que sirve
para trasladar una proteína del interior al exterior celular.
Está formado por cinco proteínas o complejos proteicos:
el complejo de reconocimiento de la señal (SRP), el receptor de
dicho complejo (receptor del SRP), el complejo proteico Sec61, la proteína
de membrana asociada al polipéptido de exportación (TRAM)
y el complejo pentaproteico con actividad peptidasa que escinde el péptido
señal.
translocator: transportador.
![]() porter.
porter.
transmembrane translocation: traslado de un lado a otro de la membrana.
transpeptidation : transpeptidación.
Reacción de hidrólisis de un enlace peptídico entre
dos aminoácidos y posterior restablecimiento del enlace entre
uno de ellos y un tercero sin gasto de energía. Son reacciones
catalizadas por peptidil-transferasas y, a veces, autocatalíticas
(es el caso de la eliminación de inteínas). Véase
intein y extein.
transporter: transportador.
![]() porter.
porter.
transposable element: elemento
transponible.
Secuencias de ADN con capacidad de mudarse de un sitio a otro de los
genomas de los organismos eucariontes y procariontes. Se distinguen varias
categorías. En los cromosomas y plásmidos de las bacterias,
por ejemplo, las hay relativamente sencillas, como las denominadas «secuencias
de inserción» (fragmento de ADN con el gen de la enzima
transposasa responsable de la transposición), y más complejos,
como son los transposones compuestos de tipo Tn, que se caracterizan
por llevar información genética adicional (por ejemplo,
genes de resistencia a fármacos), además de los genes para
la propia transposición.
Observación: Bárbara MacClintock descubrió estos
elementos en el maíz a mediados del siglo xx. Su descubrimiento,
que sólo fue reconocido años más tarde, le valió el
Premio Nobel de Fisiología y Medicina en 1983.
transposition: transposición.
1. Proceso de inserción de una copia de un elemento transponible
en otro sitio del genoma; si la copia original permanece en el sitio
de inserción primitivo se llama replicative transposition.
En cambio, si el transposón se mueve como una entidad física
de un sitio a otro sin duplicarse se llama nonreplicative transposition.
2. Movimiento de un segmento cromosómico hacia un lugar
distinto dentro del mismo o de otro cromosoma, sin intercambios recíprocos.
![]() 3. Cambio
de posición de algunos pares de bases en la misma secuencia
de ADN, por ejemplo:
3. Cambio
de posición de algunos pares de bases en la misma secuencia
de ADN, por ejemplo:
transposon: transposón.
![]() transposable
element.
transposable
element.
trans-splicing : transempalme,
empalme en trans, transayuste, ayuste en trans.
Empalme o ayuste de exones de dos transcritos primarios distintos con
la consiguiente formación de un ARNm híbrido. Véase
cis-splicing.
transversion: transversión.
![]() base-pair
substitution.
base-pair
substitution.
trigger: desencadenante,
inductor.
Dícese de la biomolécula o señal que induce o desencadena
un proceso celular.
triplet : triplete.
1 codon (codón) en el ARNm. Véase
codon.
2 anticodon (anticodón) en el ARNt. Véase
anticodon.
tRNA : ARNt.
![]() transfer
RNA.
transfer
RNA.
tRNAfMet: ARNtfMet.
![]() initiator
tRNA.
initiator
tRNA.
tRNAiMet: ARNtiMet.
![]() initiator
tRNA.
initiator
tRNA.